Дерево решений строит последовательность разбиений признакового пространства, минимизируя неоднородность узлов. Для классификации часто используют критерий Джини или энтропию . Random Forest обучает множество деревьев на бутстрап-выборках и случайных подмножествах признаков, а итоговое решение получается голосованием большинства: . Это снижает дисперсию модели и повышает обобщающую способность.
Используемые библиотеки¶
Используем numpy, pandas для работы с данными, seaborn и matplotlib для визуализации. Из sklearn — загрузчик датасета, train_test_split, классификаторы DecisionTreeClassifier и RandomForestClassifier, а также метрики классификации и построение ROC-кривых.
import numpy as np
import pandas as pd
import seaborn as sns
import matplotlib.pyplot as plt
from sklearn.datasets import load_breast_cancer
from sklearn.model_selection import (
train_test_split,
GridSearchCV,
StratifiedKFold,
validation_curve,
)
from sklearn.tree import DecisionTreeClassifier
from sklearn.ensemble import RandomForestClassifier
from sklearn.metrics import (
accuracy_score,
precision_score,
recall_score,
f1_score,
confusion_matrix,
roc_curve,
auc,
)
sns.set_theme(style="whitegrid", palette="deep")
plt.rcParams["figure.dpi"] = 120
PRIMARY_COLOR = "#1f77b4"
SECONDARY_COLOR = "#ff7f0e"
HEATMAP_CMAP = "coolwarm"
CONFUSION_CMAP = "Blues"
Датасет: описание и частичная распечатка¶
Датасет Breast Cancer Wisconsin — 569 образцов опухолей, описанных 30 числовыми признаками: средние, стандартные отклонения и экстремальные значения радиуса, текстуры, периметра, площади, гладкости клеток. Целевая переменная — target: 0 = злокачественная, 1 = доброкачественная. Задача — бинарная классификация. Классы немного несбалансированы (~37% злокачественных), поэтому используем стратификацию при разбивке.
breast = load_breast_cancer(as_frame=True)
data = breast.frame
print(f"Размерность: {data.shape}")
data.head()
Размерность: (569, 31)
Предварительная обработка¶
Отделяем признаки от целевой переменной. Разбиваем на train/test (80/20) со стратификацией — это гарантирует одинаковое соотношение классов в обоих разбиениях. Деревья решений не требуют масштабирования признаков, так как работают с пороговыми разбиениями, а не с расстояниями.
features = data.drop(columns=["target"])
target = data["target"]
X_train, X_test, y_train, y_test = train_test_split(
features, target, test_size=0.2, random_state=42, stratify=target
)
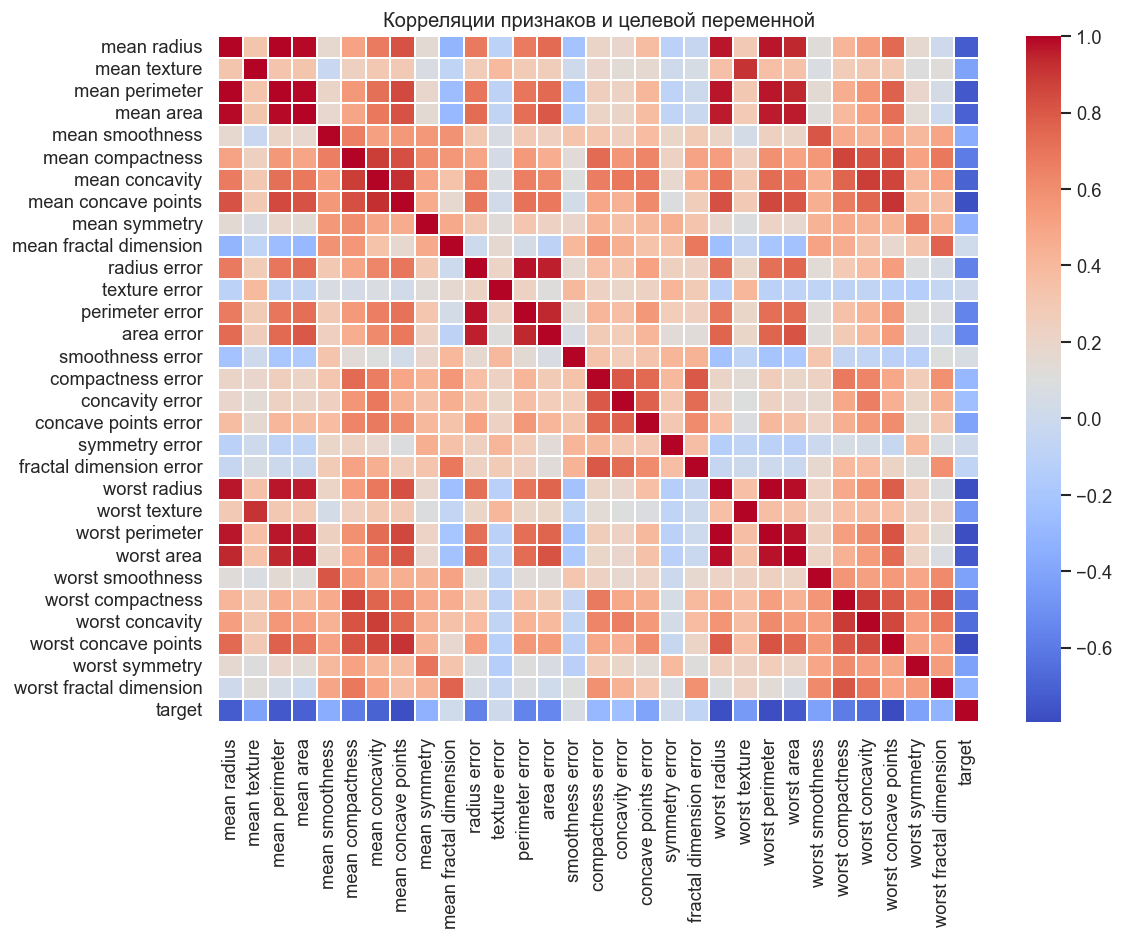
Тепловая карта корреляций¶
Матрица из 31 переменной. Заметны сильные корреляции между геометрически связанными признаками: радиус, периметр и площадь коллинеарны (). Это мультиколлинеарность — для деревьев она не критична, но полезно знать структуру данных. Признаки с яркими красными квадратами имеют наибольшую связь с целевой переменной.
plt.figure(figsize=(10, 8))
correlation = data.corr()
sns.heatmap(correlation, cmap=HEATMAP_CMAP, linewidths=0.2)
plt.title("Корреляции признаков и целевой переменной")
plt.tight_layout()
plt.show()
Обучение моделей¶
Сначала обучаем базовые модели:
DecisionTree с
max_depth=4— ограничиваем глубину для борьбы с переобучением;RandomForest из 200 деревьев — больше деревьев снижает дисперсию (закон больших чисел), но увеличивает время обучения.
Далее подберем гиперпараметры по F1 с учетом дисбаланса классов.
tree_clf = DecisionTreeClassifier(max_depth=4, random_state=42)
rf_clf = RandomForestClassifier(n_estimators=200, random_state=42)
tree_clf.fit(X_train, y_train)
rf_clf.fit(X_train, y_train)
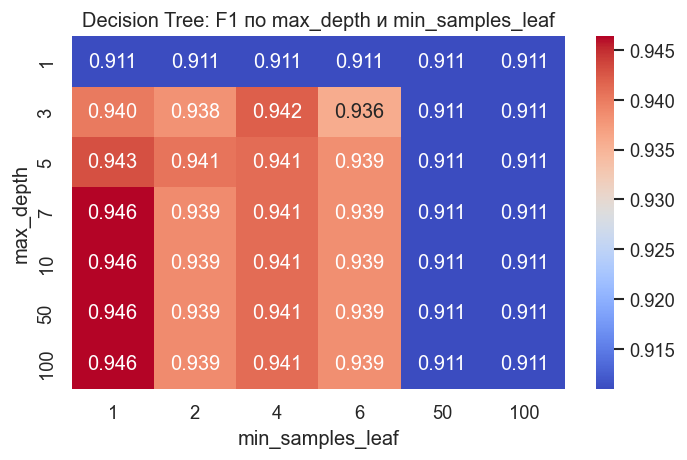
Подбор гиперпараметров (F1, быстро)¶
Используем стратифицированную кросс-валидацию и метрику F1. Для учета дисбаланса классов задаем class_weight="balanced".
cv = StratifiedKFold(n_splits=5, shuffle=True, random_state=42)
# Быстрая сетка для дерева решений
# max_depth и min_samples_leaf дают самый заметный эффект на переобучение
tree_param_grid = {
"max_depth": [1, 3, 5, 7, 10, 50, 100],
"min_samples_leaf": [1, 2, 4, 6, 50, 100],
"min_samples_split": [2, 5, 10],
}
tree_search = GridSearchCV(
DecisionTreeClassifier(random_state=42, class_weight="balanced"),
tree_param_grid,
scoring="f1",
cv=cv,
n_jobs=-1,
refit=True,
)
tree_search.fit(X_train, y_train)
print("Лучшие параметры Decision Tree:", tree_search.best_params_)
print(f"Лучшее CV F1: {tree_search.best_score_:.3f}")
Лучшие параметры Decision Tree: {'max_depth': 7, 'min_samples_leaf': 1, 'min_samples_split': 2}
Лучшее CV F1: 0.946
# Heatmap по двум параметрам при фиксированном лучшем min_samples_split
tree_results = pd.DataFrame(tree_search.cv_results_)
best_split = tree_search.best_params_["min_samples_split"]
tree_subset = tree_results[
tree_results["param_min_samples_split"] == best_split
]
tree_pivot = tree_subset.pivot_table(
index="param_max_depth",
columns="param_min_samples_leaf",
values="mean_test_score",
)
plt.figure(figsize=(6, 4))
sns.heatmap(tree_pivot, annot=True, fmt=".3f", cmap=HEATMAP_CMAP)
plt.title("Decision Tree: F1 по max_depth и min_samples_leaf")
plt.xlabel("min_samples_leaf")
plt.ylabel("max_depth")
plt.tight_layout()
plt.show()
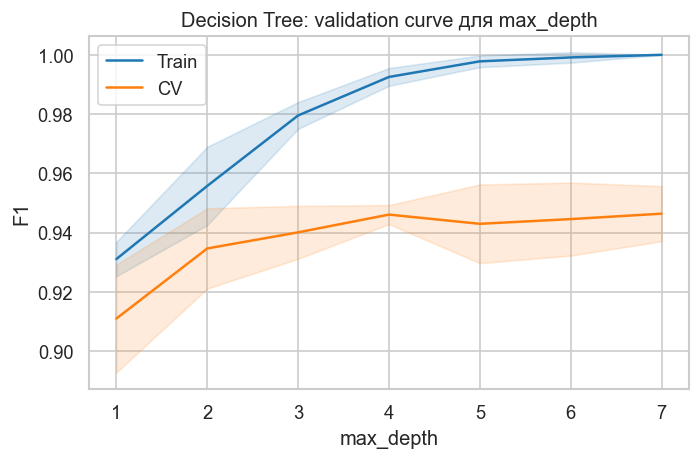
# Validation curves для дерева
def plot_validation_curve(estimator, X, y, param_name, param_range, title):
train_scores, valid_scores = validation_curve(
estimator,
X,
y,
param_name=param_name,
param_range=param_range,
scoring="f1",
cv=cv,
n_jobs=-1,
)
train_mean = train_scores.mean(axis=1)
train_std = train_scores.std(axis=1)
valid_mean = valid_scores.mean(axis=1)
valid_std = valid_scores.std(axis=1)
plt.figure(figsize=(6, 4))
plt.plot(param_range, train_mean, label="Train", color=PRIMARY_COLOR)
plt.plot(param_range, valid_mean, label="CV", color=SECONDARY_COLOR)
plt.fill_between(
param_range,
train_mean - train_std,
train_mean + train_std,
color=PRIMARY_COLOR,
alpha=0.15,
)
plt.fill_between(
param_range,
valid_mean - valid_std,
valid_mean + valid_std,
color=SECONDARY_COLOR,
alpha=0.15,
)
plt.title(title)
plt.xlabel(param_name)
plt.ylabel("F1")
plt.legend()
plt.tight_layout()
plt.show()
plot_validation_curve(
DecisionTreeClassifier(random_state=42, class_weight="balanced"),
X_train,
y_train,
param_name="max_depth",
param_range=[1, 2, 3, 4, 5, 6, 7],
title="Decision Tree: validation curve для max_depth",
)
plot_validation_curve(
DecisionTreeClassifier(random_state=42, class_weight="balanced"),
X_train,
y_train,
param_name="min_samples_leaf",
param_range=[1, 2, 4, 6, 8, 10],
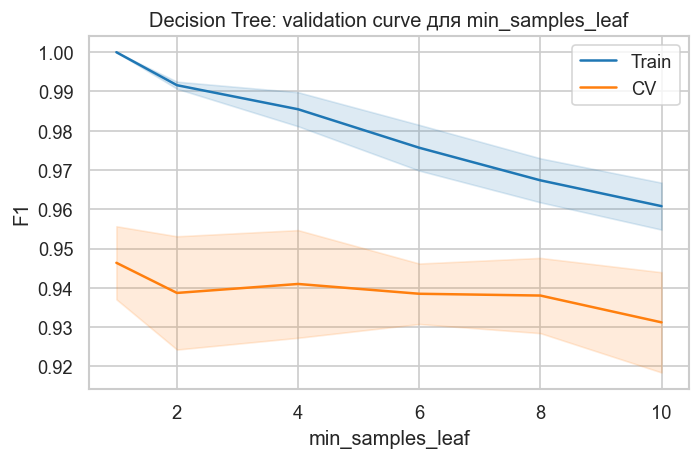
title="Decision Tree: validation curve для min_samples_leaf",
)
# Быстрая сетка для Random Forest
rf_param_grid = {
"n_estimators": [80, 120, 200, 1000],
"max_depth": [3, 5, 7, None],
"min_samples_leaf": [1, 2, 4],
"max_features": ["sqrt", "log2"],
}
rf_search = GridSearchCV(
RandomForestClassifier(random_state=42, class_weight="balanced"),
rf_param_grid,
scoring="f1",
cv=cv,
n_jobs=-1,
refit=True,
)
rf_search.fit(X_train, y_train)
print("Лучшие параметры Random Forest:", rf_search.best_params_)
print(f"Лучшее CV F1: {rf_search.best_score_:.3f}")
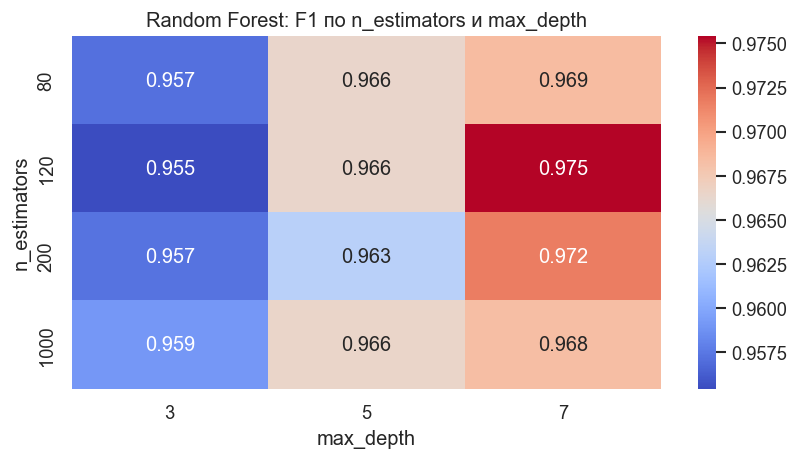
Лучшие параметры Random Forest: {'max_depth': 7, 'max_features': 'sqrt', 'min_samples_leaf': 1, 'n_estimators': 120}
Лучшее CV F1: 0.975
# Heatmap по n_estimators и max_depth при фиксированных лучших min_samples_leaf и max_features
rf_results = pd.DataFrame(rf_search.cv_results_)
best_leaf = rf_search.best_params_["min_samples_leaf"]
best_features = rf_search.best_params_["max_features"]
rf_subset = rf_results[
(rf_results["param_min_samples_leaf"] == best_leaf)
& (rf_results["param_max_features"] == best_features)
]
rf_pivot = rf_subset.pivot_table(
index="param_n_estimators",
columns="param_max_depth",
values="mean_test_score",
)
plt.figure(figsize=(7, 4))
sns.heatmap(rf_pivot, annot=True, fmt=".3f", cmap=HEATMAP_CMAP)
plt.title("Random Forest: F1 по n_estimators и max_depth")
plt.xlabel("max_depth")
plt.ylabel("n_estimators")
plt.tight_layout()
plt.show()
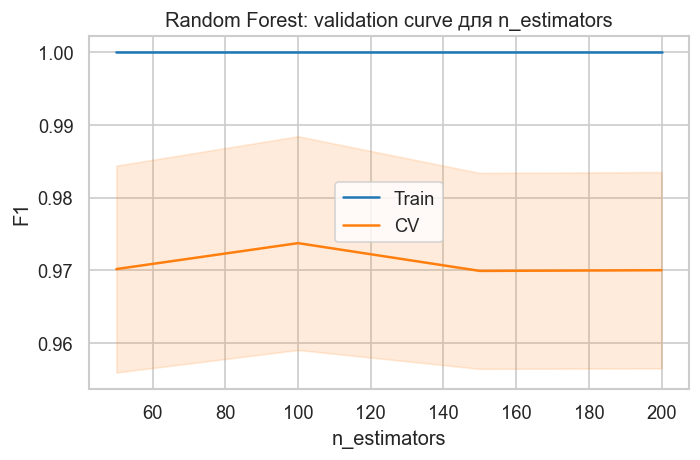
# Validation curves для Random Forest
plot_validation_curve(
RandomForestClassifier(random_state=42, class_weight="balanced"),
X_train,
y_train,
param_name="n_estimators",
param_range=[50, 100, 150, 200],
title="Random Forest: validation curve для n_estimators",
)
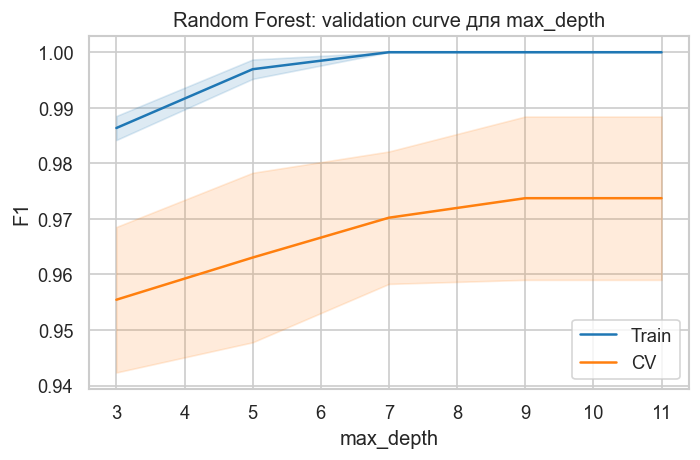
plot_validation_curve(
RandomForestClassifier(random_state=42, class_weight="balanced"),
X_train,
y_train,
param_name="max_depth",
param_range=[3, 5, 7, 9, 11],
title="Random Forest: validation curve для max_depth",
)
# Используем лучшие модели для дальнейшей оценки
tree_clf = tree_search.best_estimator_
rf_clf = rf_search.best_estimator_
Прогнозы моделей¶
Сравниваем четыре классификационные метрики для каждой модели:
Accuracy — доля верных предсказаний (может вводить в заблуждение при дисбалансе);
Precision — точность: из предсказанных положительных, сколько верных;
Recall — полнота: из всех реальных положительных, сколько нашли;
F1 — гармоническое среднее Precision и Recall.
Random Forest ожидаемо превзойдет одиночное дерево.
models = {
"Decision Tree": tree_clf,
"Random Forest": rf_clf,
}
for name, model in models.items():
preds = model.predict(X_test)
print(f"{name}")
print(f"Accuracy: {accuracy_score(y_test, preds):.3f}")
print(f"Precision: {precision_score(y_test, preds):.3f}")
print(f"Recall: {recall_score(y_test, preds):.3f}")
print(f"F1: {f1_score(y_test, preds):.3f}")
print("-")
Decision Tree
Accuracy: 0.930
Precision: 0.957
Recall: 0.931
F1: 0.944
-
Random Forest
Accuracy: 0.947
Precision: 0.958
Recall: 0.958
F1: 0.958
-
Графики выходных результатов¶
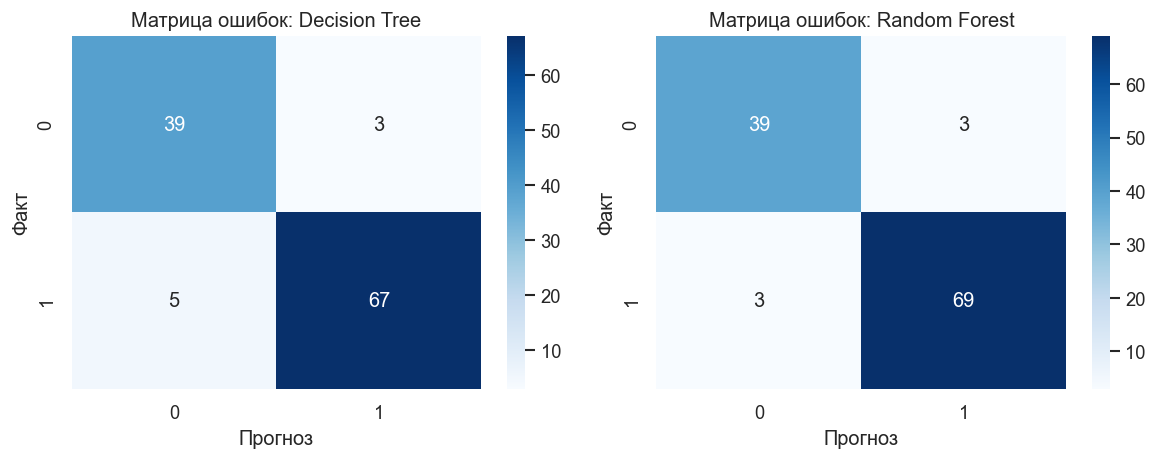
График 1. Матрицы ошибок (Confusion Matrix). Строки — истинный класс, столбцы — предсказанный. Диагональ — верные предсказания. Внедиагональные элементы: FP (ложная тревога) и FN (пропущенный злокачественный случай). В медицинских задачах FN особенно дорогостоящие.
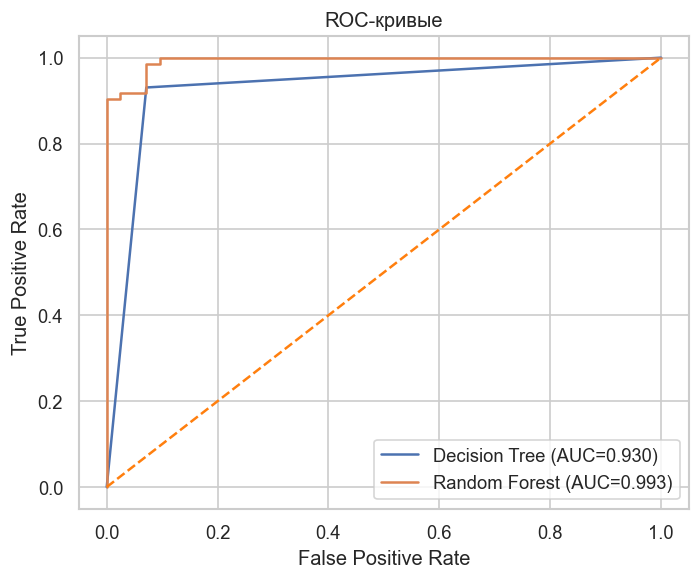
График 2. ROC-кривые. AUC (площадь под кривой) = 1 — идеальный классификатор, = 0.5 — случайный. Чем выше и левее кривая, тем лучше модель. Random Forest, как правило, дает AUC > Decision Tree.
fig, axes = plt.subplots(1, 2, figsize=(10, 4))
for ax, (name, model) in zip(axes, models.items()):
cm = confusion_matrix(y_test, model.predict(X_test))
sns.heatmap(cm, annot=True, fmt="d", cmap=CONFUSION_CMAP, ax=ax)
ax.set_title(f"Матрица ошибок: {name}")
ax.set_xlabel("Прогноз")
ax.set_ylabel("Факт")
plt.tight_layout()
plt.show()
plt.figure(figsize=(6, 5))
colors = sns.color_palette("deep", n_colors=len(models))
for (name, model), color in zip(models.items(), colors):
proba = model.predict_proba(X_test)[:, 1]
fpr, tpr, _ = roc_curve(y_test, proba)
roc_auc = auc(fpr, tpr)
plt.plot(fpr, tpr, label=f"{name} (AUC={roc_auc:.3f})", color=color)
plt.plot([0, 1], [0, 1], color=SECONDARY_COLOR, linestyle="--")
plt.xlabel("False Positive Rate")
plt.ylabel("True Positive Rate")
plt.title("ROC-кривые")
plt.legend()
plt.tight_layout()
plt.show()